如何快速掌握单细胞分析:CELLxGENE新手必看的3个实用技巧
news2026/3/31 2:29:36
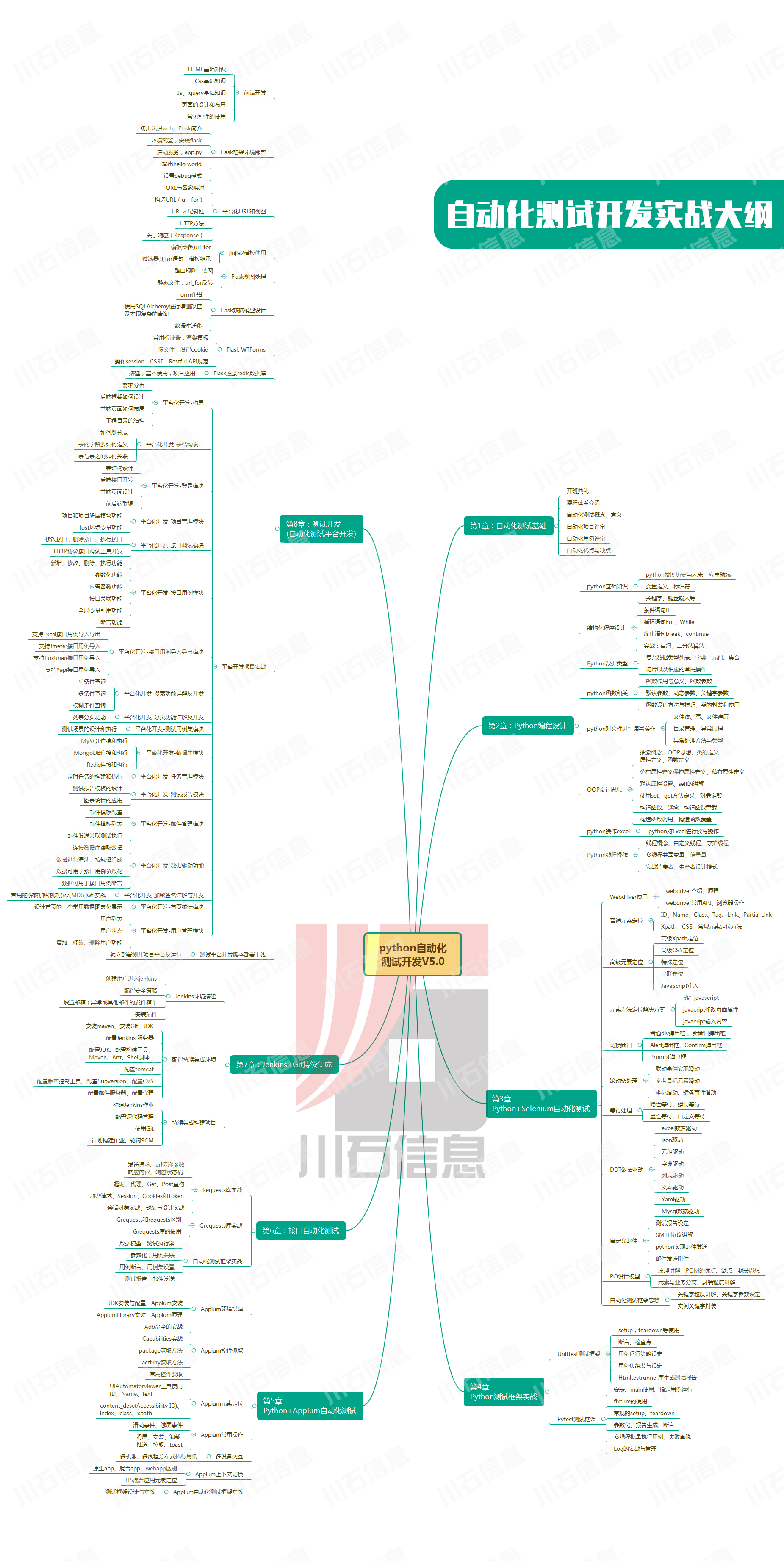
如何快速掌握单细胞分析CELLxGENE新手必看的3个实用技巧【免费下载链接】cellxgeneAn interactive explorer for single-cell transcriptomics data项目地址: https://gitcode.com/gh_mirrors/ce/cellxgene你是否曾经面对海量的单细胞转录组数据感到无从下手想要探索细胞间的异质性却不知从何开始今天我将为你介绍一款革命性的工具——CELLxGENE它能让你在几分钟内从数据小白变身为单细胞分析高手这款由Chan Zuckerberg Initiative开发的交互式数据探索器专为单细胞转录组数据分析而生无论你是生物信息学新手还是经验丰富的研究人员都能轻松上手。问题一单细胞数据可视化太复杂CELLxGENE让你一目了然想象一下你刚刚完成单细胞RNA测序获得了数千甚至上百万个细胞的表达数据。传统的分析方法需要编写复杂的代码使用R或Python进行数据处理和可视化这个过程既耗时又容易出错。CELLxGENE的解决方案只需一个命令你就能启动一个完整的交互式数据探索平台。安装完成后运行以下命令即可开始你的单细胞探索之旅pip install cellxgene cellxgene launch https://cellxgene-example-data.czi.technology/pbmc3k.h5ad这个简单的命令背后CELLxGENE为你搭建了一个完整的分析环境。它会自动处理数据格式转换、降维计算和可视化渲染让你专注于科学发现而非技术细节。上图展示了CELLxGENE的初始界面你可以看到左侧细胞分类导航帮助你快速筛选感兴趣的细胞群体中央细胞在降维空间中的分布如UMAP或t-SNE直观展示细胞间的相似性和差异性右侧质量控制面板显示基因数量、线粒体百分比等关键指标问题二如何从海量基因中找到关键信息交互式筛选来帮忙在单细胞数据分析中最常遇到的问题就是信息过载。面对成千上万的基因和细胞如何快速找到与研究问题相关的关键信息CELLxGENE的智能筛选功能通过交叉筛选crossfiltering技术CELLxGENE让你能够像使用电商网站筛选商品一样轻松筛选细胞数据。这个动态演示展示了CELLxGENE的强大筛选能力多维度联动选择一个细胞类型其他所有图表都会实时更新即时反馈筛选条件立即生效无需等待计算视觉引导颜色编码和直方图帮助你理解数据分布你可以基于以下条件进行筛选细胞类型或聚类结果特定基因的表达水平质量控制指标如线粒体基因比例自定义的细胞注释标签问题三如何快速发现差异表达基因CELLxGENE的基因表达分析差异表达分析是单细胞研究的核心但传统的分析方法需要复杂的统计计算和多次数据转换。CELLxGENE将这个过程变得异常简单。实时基因表达可视化只需点击基因名称你就能立即看到该基因在所有细胞中的表达模式。观察上图你会发现颜色编码基因表达水平通过颜色深浅直观表示空间分布高表达细胞在降维图中的位置一目了然统计信息右侧直方图显示基因表达的总体分布差异表达分析更简单想要比较两个细胞群体间的基因表达差异CELLxGENE内置的差异表达分析功能让你无需编写任何代码就能获得统计结果。这个功能特别适合发现标志物基因识别特定细胞类型的特征基因验证假设比较不同处理条件下的基因表达变化功能注释根据差异表达基因推测细胞功能实用技巧一5分钟完成安装与配置环境准备CELLxGENE支持Python 3.10及以上版本。如果你还没有合适的Python环境建议使用conda或virtualenv创建独立环境python --version # 检查Python版本 python -m venv cellxgene_env # 创建虚拟环境 source cellxgene_env/bin/activate # 激活环境Linux/Mac一键安装安装过程简单到只需一行命令pip install cellxgene这个命令会自动安装所有必要的依赖包括数据处理后端基于Flask框架前端可视化组件数据格式转换工具统计分析库启动你的第一个分析安装完成后你可以立即开始分析示例数据# 使用在线示例数据 cellxgene launch https://cellxgene-example-data.czi.technology/pbmc3k.h5ad # 或者使用本地数据 cellxgene launch /path/to/your/data.h5ad系统会自动在浏览器中打开分析界面地址通常是 http://localhost:5005。实用技巧二数据导入的3种方法1. 使用示例数据快速上手项目提供了完整的示例数据集位于 example-dataset/ 目录。这些数据已经过预处理可以直接用于分析。2. 导入自己的h5ad文件如果你的数据已经是AnnData格式h5ad文件那么导入过程非常简单cellxgene launch your_data.h5adCELLxGENE会自动识别数据结构包括细胞注释信息obs基因表达矩阵X基因注释信息var降维嵌入obsm3. 数据预处理指南如果你的数据还不是h5ad格式可以使用scanpy等工具进行转换。CELLxGENE要求数据满足以下基本结构表达矩阵稀疏或稠密矩阵细胞注释至少包含细胞标识符可选降维坐标UMAP、t-SNE等实用技巧三高级功能深度挖掘嵌入空间切换不同的降维算法可能揭示数据的不同特征。CELLxGENE支持在多种嵌入空间之间无缝切换你可以比较UMAP通常能更好地保持全局结构t-SNE擅长展示局部相似性PCA线性降维计算速度快类别分解分析想要深入了解特定细胞群体的内部结构CELLxGENE的类别分解功能让你能够深入分析每个亚群这个功能特别适合验证聚类结果的合理性发现亚群内部的异质性识别过渡状态的细胞基因比较分析需要同时观察多个基因的表达模式CELLxGENE的基因比较功能让你能够并排分析多个基因通过这个功能你可以发现共表达基因模块识别相互排斥的表达模式验证基因间的相关性技术架构解析了解CELLxGENE的内部机制CELLxGENE采用了现代化的技术架构确保在处理大规模数据时依然保持流畅的性能后端架构核心后端逻辑位于 server/app/基于Flask框架构建提供RESTful API接口。主要功能包括数据加载和预处理查询处理和响应用户会话管理安全性和访问控制前端架构前端组件位于client/src/components/采用React和Redux架构提供交互式可视化界面实时数据更新用户状态管理响应式设计数据处理流程数据加载从h5ad文件读取数据格式转换转换为内部数据结构查询处理响应用户的筛选和查询请求可视化渲染生成交互式图表常见问题与解决方案Q: CELLxGENE能处理多大的数据集A: CELLxGENE经过优化可以处理至少100万个细胞的数据集。性能取决于你的硬件配置特别是内存大小。Q: 如何保存分析结果A: CELLxGENE支持多种导出方式截图保存可视化结果导出筛选后的细胞子集保存差异表达分析结果Q: 可以自定义分析流程吗A: 是的CELLxGENE提供了丰富的API接口你可以通过编程方式扩展功能或集成到自己的分析流程中。Q: 如何获得技术支持A: 你可以查阅官方文档获取详细指南加入CZI Science Community Slack的#cellxgene-users频道在GitHub仓库提交问题报告开始你的单细胞探索之旅现在你已经掌握了CELLxGENE的核心功能和实用技巧。这款工具的设计初衷就是降低单细胞数据分析的门槛让研究人员能够专注于科学发现而非技术细节。立即行动安装CELLxGENE只需一行命令加载示例数据体验完整的分析流程导入自己的数据开始真正的科研探索记住最好的学习方式就是动手实践。CELLxGENE的交互式界面让你能够实时看到分析结果立即获得反馈。无论你是要验证一个假设、探索新的细胞类型还是仅仅想了解单细胞数据的奥秘CELLxGENE都是你的理想伙伴。生物学研究正在经历一场数据革命单细胞技术为我们打开了观察生命微观世界的新窗口。CELLxGENE就是这个窗口的放大镜让你能够清晰地看到每一个细胞的独特故事。现在就开始你的单细胞探索之旅吧【免费下载链接】cellxgeneAn interactive explorer for single-cell transcriptomics data项目地址: https://gitcode.com/gh_mirrors/ce/cellxgene创作声明:本文部分内容由AI辅助生成(AIGC),仅供参考
本文来自互联网用户投稿,该文观点仅代表作者本人,不代表本站立场。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如若转载,请注明出处:http://www.coloradmin.cn/o/2466981.html
如若内容造成侵权/违法违规/事实不符,请联系多彩编程网进行投诉反馈,一经查实,立即删除!相关文章
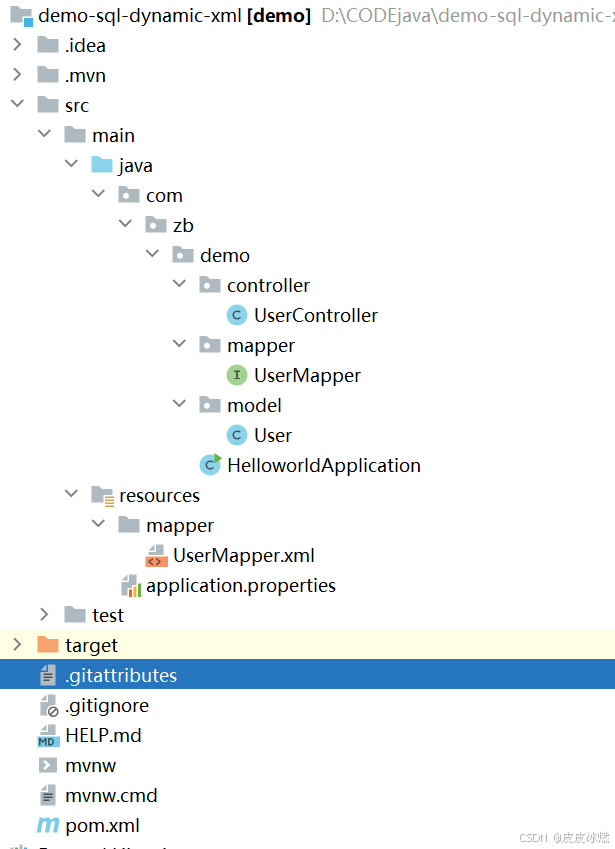
SpringBoot-17-MyBatis动态SQL标签之常用标签
文章目录 1 代码1.1 实体User.java1.2 接口UserMapper.java1.3 映射UserMapper.xml1.3.1 标签if1.3.2 标签if和where1.3.3 标签choose和when和otherwise1.4 UserController.java2 常用动态SQL标签2.1 标签set2.1.1 UserMapper.java2.1.2 UserMapper.xml2.1.3 UserController.ja…
wordpress后台更新后 前端没变化的解决方法
使用siteground主机的wordpress网站,会出现更新了网站内容和修改了php模板文件、js文件、css文件、图片文件后,网站没有变化的情况。
不熟悉siteground主机的新手,遇到这个问题,就很抓狂,明明是哪都没操作错误&#x…
网络编程(Modbus进阶)
思维导图 Modbus RTU(先学一点理论)
概念 Modbus RTU 是工业自动化领域 最广泛应用的串行通信协议,由 Modicon 公司(现施耐德电气)于 1979 年推出。它以 高效率、强健性、易实现的特点成为工业控制系统的通信标准。 包…
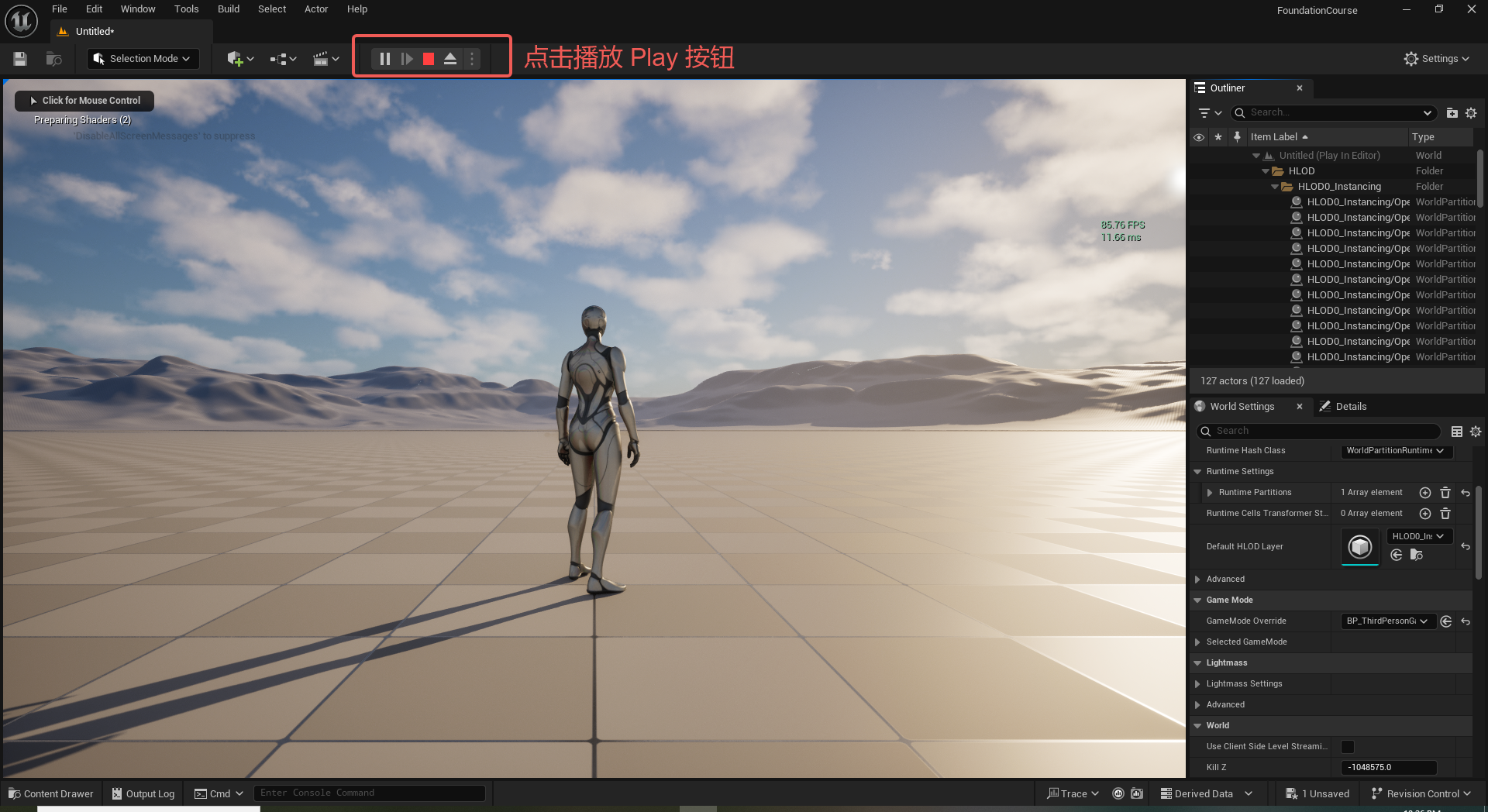
UE5 学习系列(二)用户操作界面及介绍
这篇博客是 UE5 学习系列博客的第二篇,在第一篇的基础上展开这篇内容。博客参考的 B 站视频资料和第一篇的链接如下:
【Note】:如果你已经完成安装等操作,可以只执行第一篇博客中 2. 新建一个空白游戏项目 章节操作,重…
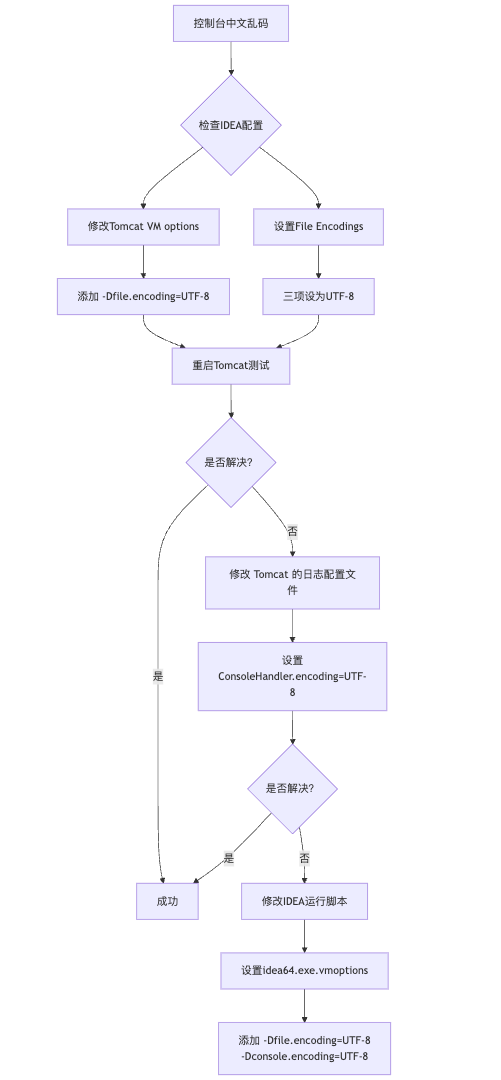
IDEA运行Tomcat出现乱码问题解决汇总
最近正值期末周,有很多同学在写期末Java web作业时,运行tomcat出现乱码问题,经过多次解决与研究,我做了如下整理:
原因:
IDEA本身编码与tomcat的编码与Windows编码不同导致,Windows 系统控制台…
利用最小二乘法找圆心和半径
#include <iostream>
#include <vector>
#include <cmath>
#include <Eigen/Dense> // 需安装Eigen库用于矩阵运算 // 定义点结构
struct Point { double x, y; Point(double x_, double y_) : x(x_), y(y_) {}
}; // 最小二乘法求圆心和半径 …
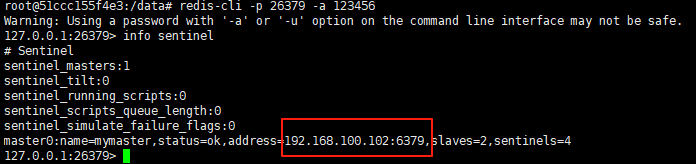
使用docker在3台服务器上搭建基于redis 6.x的一主两从三台均是哨兵模式
一、环境及版本说明
如果服务器已经安装了docker,则忽略此步骤,如果没有安装,则可以按照一下方式安装: 1. 在线安装(有互联网环境): 请看我这篇文章 传送阵>> 点我查看 2. 离线安装(内网环境):请看我这篇文章 传送阵>> 点我查看
说明:假设每台服务器已…
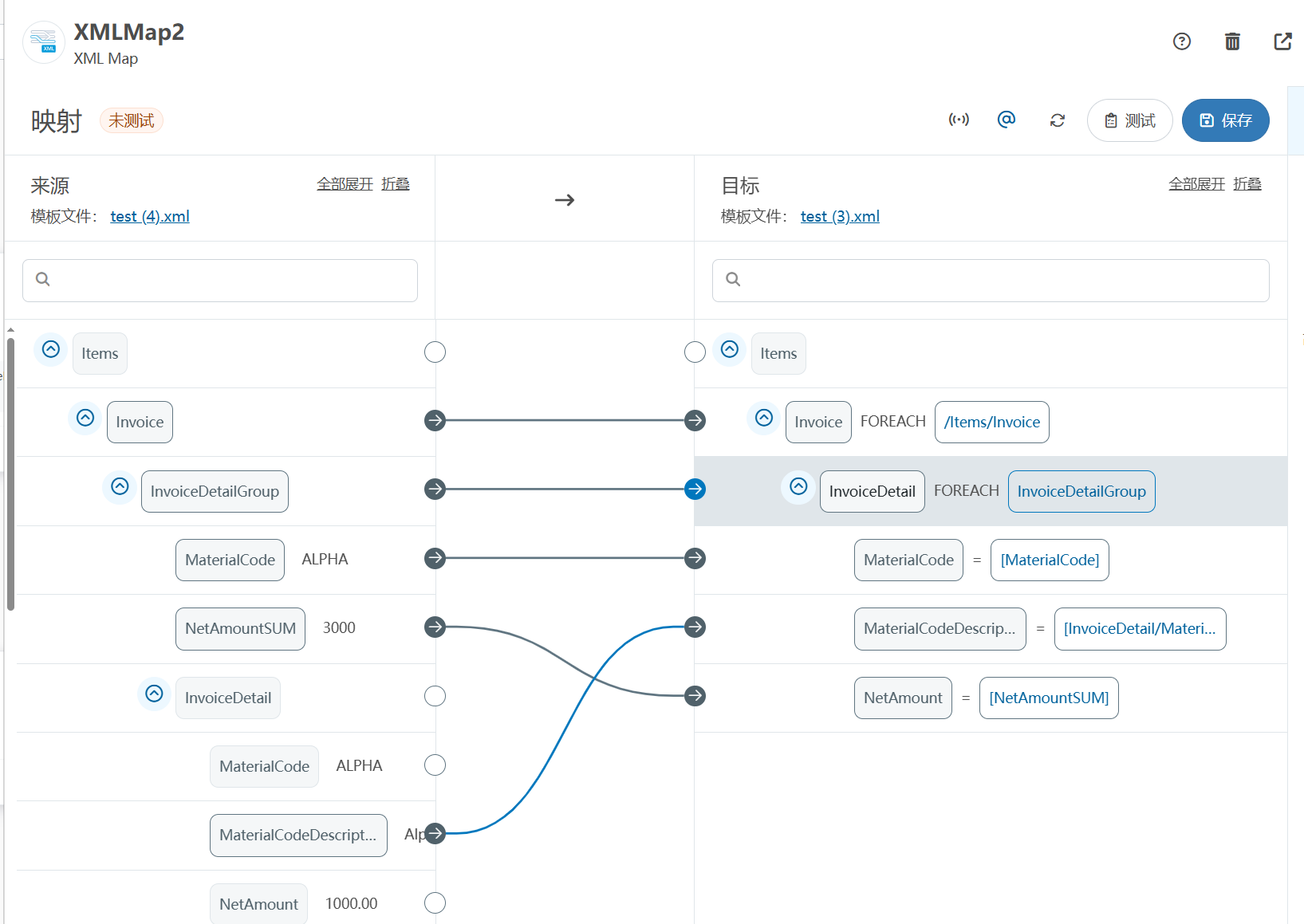
XML Group端口详解
在XML数据映射过程中,经常需要对数据进行分组聚合操作。例如,当处理包含多个物料明细的XML文件时,可能需要将相同物料号的明细归为一组,或对相同物料号的数量进行求和计算。传统实现方式通常需要编写脚本代码,增加了开…
LBE-LEX系列工业语音播放器|预警播报器|喇叭蜂鸣器的上位机配置操作说明
LBE-LEX系列工业语音播放器|预警播报器|喇叭蜂鸣器专为工业环境精心打造,完美适配AGV和无人叉车。同时,集成以太网与语音合成技术,为各类高级系统(如MES、调度系统、库位管理、立库等)提供高效便捷的语音交互体验。
L…
(LeetCode 每日一题) 3442. 奇偶频次间的最大差值 I (哈希、字符串)
题目:3442. 奇偶频次间的最大差值 I 思路 :哈希,时间复杂度0(n)。 用哈希表来记录每个字符串中字符的分布情况,哈希表这里用数组即可实现。
C版本:
class Solution {
public:int maxDifference(string s) {int a[26]…
【大模型RAG】拍照搜题技术架构速览:三层管道、两级检索、兜底大模型
摘要
拍照搜题系统采用“三层管道(多模态 OCR → 语义检索 → 答案渲染)、两级检索(倒排 BM25 向量 HNSW)并以大语言模型兜底”的整体框架: 多模态 OCR 层 将题目图片经过超分、去噪、倾斜校正后,分别用…
【Axure高保真原型】引导弹窗
今天和大家中分享引导弹窗的原型模板,载入页面后,会显示引导弹窗,适用于引导用户使用页面,点击完成后,会显示下一个引导弹窗,直至最后一个引导弹窗完成后进入首页。具体效果可以点击下方视频观看或打开下方…
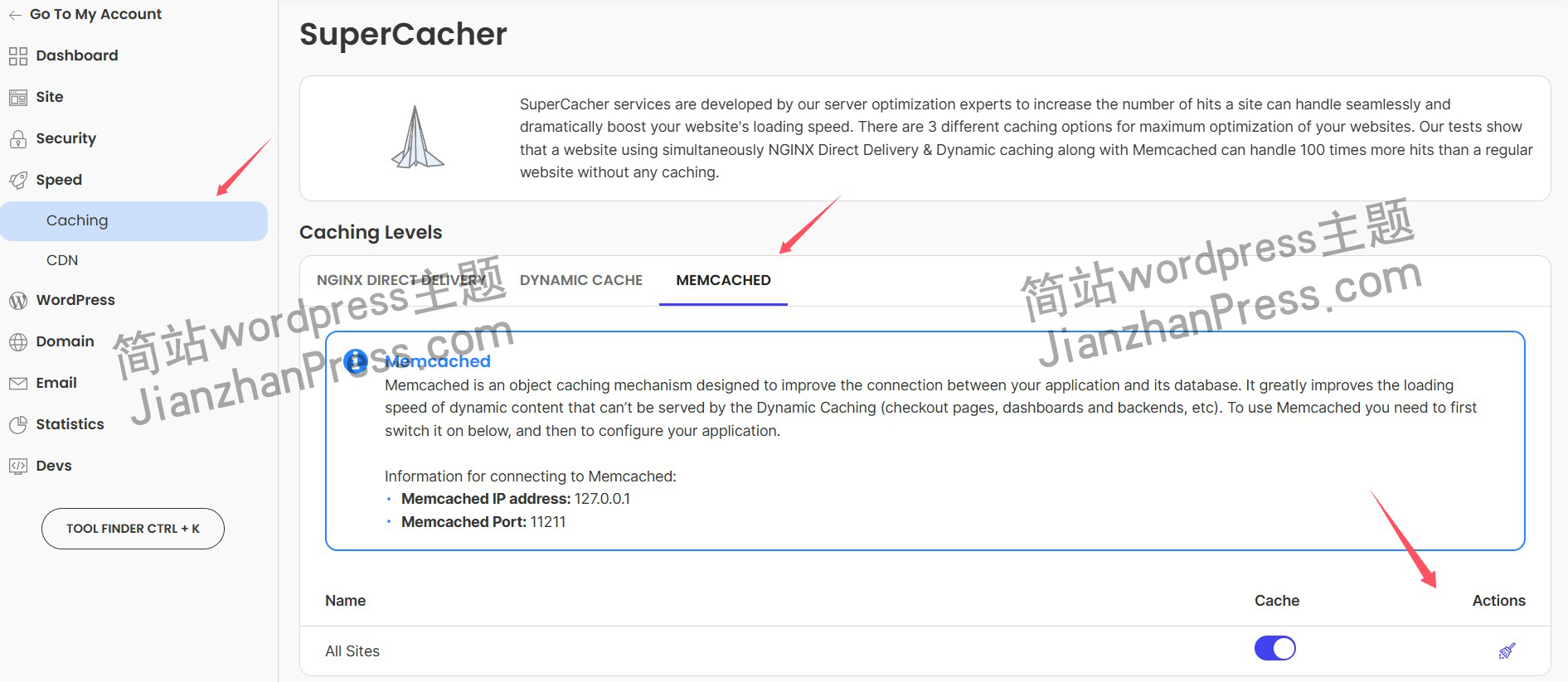
接口测试中缓存处理策略
在接口测试中,缓存处理策略是一个关键环节,直接影响测试结果的准确性和可靠性。合理的缓存处理策略能够确保测试环境的一致性,避免因缓存数据导致的测试偏差。以下是接口测试中常见的缓存处理策略及其详细说明:
一、缓存处理的核…
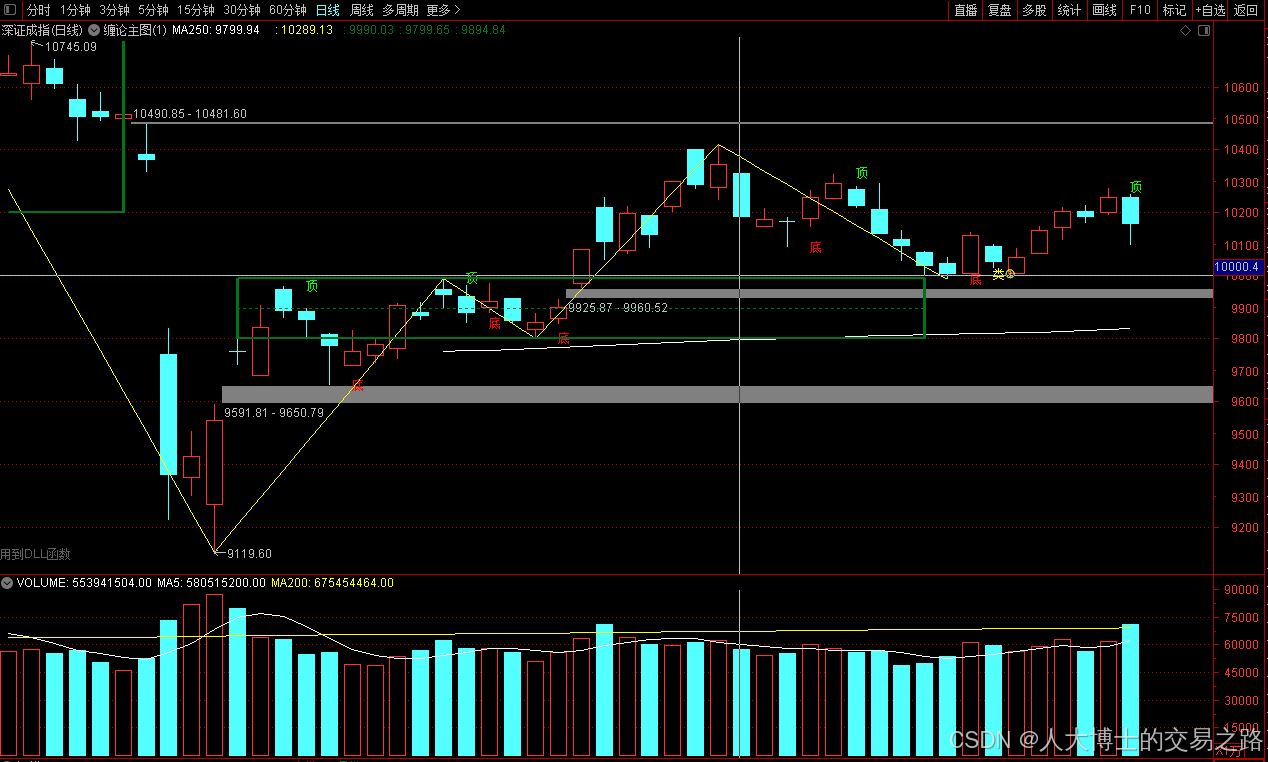
龙虎榜——20250610
上证指数放量收阴线,个股多数下跌,盘中受消息影响大幅波动。 深证指数放量收阴线形成顶分型,指数短线有调整的需求,大概需要一两天。 2025年6月10日龙虎榜行业方向分析 1. 金融科技
代表标的:御银股份、雄帝科技
驱动…
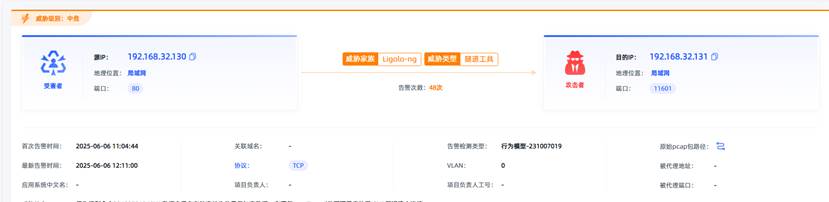
观成科技:隐蔽隧道工具Ligolo-ng加密流量分析
1.工具介绍
Ligolo-ng是一款由go编写的高效隧道工具,该工具基于TUN接口实现其功能,利用反向TCP/TLS连接建立一条隐蔽的通信信道,支持使用Let’s Encrypt自动生成证书。Ligolo-ng的通信隐蔽性体现在其支持多种连接方式,适应复杂网…
铭豹扩展坞 USB转网口 突然无法识别解决方法
当 USB 转网口扩展坞在一台笔记本上无法识别,但在其他电脑上正常工作时,问题通常出在笔记本自身或其与扩展坞的兼容性上。以下是系统化的定位思路和排查步骤,帮助你快速找到故障原因:
背景:
一个M-pard(铭豹)扩展坞的网卡突然无法识别了,扩展出来的三个USB接口正常。…
未来机器人的大脑:如何用神经网络模拟器实现更智能的决策?
编辑:陈萍萍的公主一点人工一点智能 未来机器人的大脑:如何用神经网络模拟器实现更智能的决策?RWM通过双自回归机制有效解决了复合误差、部分可观测性和随机动力学等关键挑战,在不依赖领域特定归纳偏见的条件下实现了卓越的预测准…
Linux应用开发之网络套接字编程(实例篇)
服务端与客户端单连接
服务端代码
#include <sys/socket.h>
#include <sys/types.h>
#include <netinet/in.h>
#include <stdio.h>
#include <stdlib.h>
#include <string.h>
#include <arpa/inet.h>
#include <pthread.h>
…
华为云AI开发平台ModelArts
华为云ModelArts:重塑AI开发流程的“智能引擎”与“创新加速器”!
在人工智能浪潮席卷全球的2025年,企业拥抱AI的意愿空前高涨,但技术门槛高、流程复杂、资源投入巨大的现实,却让许多创新构想止步于实验室。数据科学家…
深度学习在微纳光子学中的应用
深度学习在微纳光子学中的主要应用方向
深度学习与微纳光子学的结合主要集中在以下几个方向:
逆向设计 通过神经网络快速预测微纳结构的光学响应,替代传统耗时的数值模拟方法。例如设计超表面、光子晶体等结构。
特征提取与优化 从复杂的光学数据中自…