Pharma RAG:企业知识库的架构革命
news2026/5/15 15:50:22
一、为什么制药行业的知识库问题比你想的严重一名医学写作(Medical Writer)在准备 CTD 5.3.5.1(临床研究报告摘要)时,需要交叉引用:3 份 Phase III CSR(临床研究报告),每份 800–2000 页协议书修正案 5 个版本统计分析报告(SAP)+ 列表表格(TLF)共 1200 张竞品公开文献 40+ 篇内部 SOP 和监管对应文件若干在没有 AI 的情况下,熟练的 MW 完成这个任务需要3–5 天。用传统企业搜索(Elasticsearch / SharePoint 全文索引)?省下来的顶多是找文件的时间,文档本身还是得一页页读。这不是效率问题,是认知负荷问题。而 RAG 真正解决的,正是这个。二、RAG 的本质:不是搜索引擎升级,是知识架构重建很多人把 RAG 理解为"更聪明的搜索",这个理解差了一个维度。传统搜索的逻辑是:匹配词 → 返回文档。用户还是要自己读文档,自己综合,自己判断。RAG 的逻辑是:理解意图 → 精准定位段落 → 合成答案 → 提供引用。用户得到的是结论,而不是文档列表。制药场景的特殊性在于三点:1. 文档密度极高,同义词体系复杂一个药物在不同文件里可能叫:通用名 / INN / 商品名 / 化合物编号 / CAS号 / 研发代号。传统关键词检索在这里基本失效——你搜 “gefitinib”,搜不到写着 “ZD1839” 的段落。2. 跨文档推理是刚需“这个化合物在 Phase II 的 ORR 是多少,Phase III 里有没有变化,原因是什么?”——这个问题的答案分散在两份 CSR 的不同章节里,没有跨文档推理能力的系统无法回答。3. 可追溯性是监管要求,不是产品特性FDA 的电子提交规范要求所有数据来源可追溯。AI 生成的任何结论,必须能定位到原始文档的具体段落。这不是可选项。三、全链路架构设计:从文档入库到答案生成经过两年在多个药企项目的迭代,我们沉淀出一套三层架构:离线摄入 Pipeline → 在线查询 Pipeline → 持续评估与监控。离线摄入的几个关键决策:解析层:PDF 不等于文本。制药 CSR 里充满了多列表格、脚注、图表标注。我们用 Unstructured.io + 自研后处理来处理结构,纯 PyPDF2 提出来的文本在 CSR 场景误差率高达 30%+。分块层:后面单独讲,这里是最容易被低估的环节。向量化层:通用 Embedding 模型在生物医药领域效果有明显 Gap。PubMedBERT 或经过领域微调的模型,在制药文档的检索召回率上比 text-embedding-ada-002 高出 15–20 个百分点。混合索引:只用向量检索会丢失精确匹配(药物编号、p 值、剂量数值)。向量 + BM25 的 RRF 融合是目前最稳健的组合。在线查询的关键设计:P99 延迟控制在 2s 以内,这是用户可接受的临界值。我们的拆解是:查询改写: 300ms(小模型或规则)向量检索: 200ms(ANN 近似搜索)Rerank: 400ms(Cross-Encoder,Top-K=20 → Top-K=5)LLM 生成: 1000ms(Streaming 输出,体感更快)四、最被低估的环节:Pharma 文档的分块策略90% 的 RAG 项目在这里踩坑,然后把问题归因到"模型不行"或"数据不好"。我们在制药场景的最终方案是父子层级分块(Parent-Child Chunking):核心思路:用小块做检索(256–512 tokens,精准),命中后返回父块(1024–2048 tokens,上下文完整)。这解决了 RAG 的核心张力:检索需要小粒度(精准),生成需要大粒度(上下文)。对于 CSR 这类高度结构化的文档,我们额外加了章节元数据:每个 Chunk 携带section_path(如 “5.3.5.1 §3.2 药效学 主要终点”),检索时可以按章节过滤,也可以在引用里精确标注来源位置。五、代码实战:核心模块完整实现5.1 文档摄入 Pipeline# pharma_ingestion.py — 制药文档摄入 Pipeline(已脱敏)# 依赖:unstructured, langchain, weaviate-client, sentence-transformersimporthashlibimportloggingfromdataclassesimportdataclass,fieldfrompathlibimportPathfromtypingimportAnyimportweaviatefromlangchain.text_splitterimportRecursiveCharacterTextSplitterfromsentence_transformersimportSentenceTransformerfromunstructured.partition.pdfimportpartition_pdf logger=logging.getLogger("pharma_ingestion")@dataclassclassPharmaDocMeta:"""制药文档元数据——驱动权限过滤和引用生成"""doc_id:strdoc_type:str# CSR | SCS | Protocol | IB | SOP | Labeltitle:strversion:streffective_date:strindication:list[str]# 适应症列表molecule:str# 分子/化合物study_phase:str# Phase I/II/III/IVclassification:str# CONFIDENTIAL | INTERNAL | PUBLICowner_dept:str@dataclassclassChunk:"""单个文本块,携带完整溯源信息"""chunk_id:strparent_id:str# 父块 ID(父子分块用)text:strsection_path:str# e.g. "§3.2 Primary Endpoint"page_range:tuple[int,int]meta:PharmaDocMeta embedding:list[float]=field(default_factory=list)classPharmaDocumentParser:""" 制药文档解析器 处理 CSR/SCS/Protocol 的特殊结构:多列表格、脚注、图表引用 """def__init__(self,strategy:str="hi_res"):# hi_res 模式:调用 OCR + 版面分析,适合扫描件和复杂表格# fast 模式:纯文本提取,适合已结构化的 DOCXself.strategy=strategydefparse(self,file_path:Path)-list[dict]:"""返回结构化元素列表(文本段落 / 表格 / 标题)"""elements=partition_pdf(filename=str(file_path),strategy=self.strategy,infer_table_structure=True,# 表格结构识别include_page_breaks=True,)structured=[]foreleminelements:elem_type=type(elem).__name__# Title / NarrativeText / Table etc.structured.append({"type":elem_type,"text":str(elem),"page":getattr(elem.metadata,"page_number",None),"is_table":elem_type=="Table",})returnstructuredclassParentChildChunker:""" 父子层级分块器 - 父块(2048 tok):存储,用于生成时的上下文 - 子块(256 tok):用于精准向量检索 制药场景强烈推荐此模式 """def__init__(self,parent_chunk_size:int=2048,child_chunk_size:int=256,child_overlap:int=32,):self.parent_splitter=RecursiveCharacterTextSplitter(chunk_size=parent_chunk_size,chunk_overlap=128,separators=["\n\n\n","\n\n","\n","。",". "],)self.child_splitter=RecursiveCharacterTextSplitter(chunk_size=child_chunk_size,chunk_overlap=child_overlap,separators=["\n\n","\n","。",". "," "],)defsplit(self,elements:list[dict],meta:PharmaDocMeta)-list[Chunk]:""" 输入解析后的元素列表,输出父子 Chunk 列表 表格元素:整体作为一个 Chunk 不拆分 """chunks:list[Chunk]=[]current_section="§ Unknown"text_buffer=[]page_start=1foreleminelements:# 更新章节路径ifelem["type"]=="Title":current_section=elem["text"].strip()continue# 表格:整体保留,不拆分ifelem["is_table"]:table_chunk=self._make_chunk(text=elem["text"],section_path=current_section,page_range=(elem.get("page",0),elem.get("page",0)),meta=meta,parent_id="",# 表格块本身就是原子单元)chunks.append(table_chunk)continuetext_buffer.append(elem["text"])# 处理剩余文本缓冲full_text="\n\n".join(text_buffer)parent_texts=self.parent_splitter.split_text(full_text)forp_textinparent_texts:parent_chunk=self._make_chunk(text=p_text,section_path=current_section,page_range=(page_start,page_start),meta=meta,parent_id="",)chunks.append(parent_chunk)# 为每个父块生成子块(用于检索)child_texts=self.child_splitter.split_text(p_text)forc_textinchild_texts:child_chunk=self._make_chunk(text=c_text,section_path=current_section,page_range=(page_start,page_start),meta=meta,parent_id=parent_chunk.chunk_id,)chunks.append(child_chunk)returnchunksdef_make_chunk(self,text:str,section_path:str,page_range:tuple,meta:PharmaDocMeta,parent_id:str,)-Chunk:chunk_id=hashlib.sha256(f"{meta.doc_id}:{text[:128]}".encode()).hexdigest()[:16]returnChunk(chunk_id=chunk_id,parent_id=parent_id,text=text,section_path=section_path,page_range=page_range,meta=meta,)classPharmaEmbedder:""" 制药领域向量化 强烈建议使用领域预训练模型,而非通用 OpenAI Embedding 实测:PubMedBERT-fine-tuned 在 CSR 检索上比 ada-002 高 18pp recall """def__init__(self,model_name:str="pritamdeka/PubMedBERT-mnli-snli-scinli"):self.model=SentenceTransformer(model_name)logger.info(f"Embedder loaded:{model_name}")defembed_batch(self,texts:list[str],batch_size:int=64)-list[list[float]]:"""批量向量化,自动分批处理"""all_embeddings=[]foriinrange(0,len(texts),batch_size):batch=texts[i:i+batch_size]embeddings=self.model.encode(batch,normalize_embeddings=True,# 余弦相似度需要归一化show_progress_bar=False,)all_em
本文来自互联网用户投稿,该文观点仅代表作者本人,不代表本站立场。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如若转载,请注明出处:http://www.coloradmin.cn/o/2508128.html
如若内容造成侵权/违法违规/事实不符,请联系多彩编程网进行投诉反馈,一经查实,立即删除!相关文章
SpringBoot-17-MyBatis动态SQL标签之常用标签
文章目录 1 代码1.1 实体User.java1.2 接口UserMapper.java1.3 映射UserMapper.xml1.3.1 标签if1.3.2 标签if和where1.3.3 标签choose和when和otherwise1.4 UserController.java2 常用动态SQL标签2.1 标签set2.1.1 UserMapper.java2.1.2 UserMapper.xml2.1.3 UserController.ja…
wordpress后台更新后 前端没变化的解决方法
使用siteground主机的wordpress网站,会出现更新了网站内容和修改了php模板文件、js文件、css文件、图片文件后,网站没有变化的情况。
不熟悉siteground主机的新手,遇到这个问题,就很抓狂,明明是哪都没操作错误&#x…
网络编程(Modbus进阶)
思维导图 Modbus RTU(先学一点理论)
概念 Modbus RTU 是工业自动化领域 最广泛应用的串行通信协议,由 Modicon 公司(现施耐德电气)于 1979 年推出。它以 高效率、强健性、易实现的特点成为工业控制系统的通信标准。 包…
UE5 学习系列(二)用户操作界面及介绍
这篇博客是 UE5 学习系列博客的第二篇,在第一篇的基础上展开这篇内容。博客参考的 B 站视频资料和第一篇的链接如下:
【Note】:如果你已经完成安装等操作,可以只执行第一篇博客中 2. 新建一个空白游戏项目 章节操作,重…
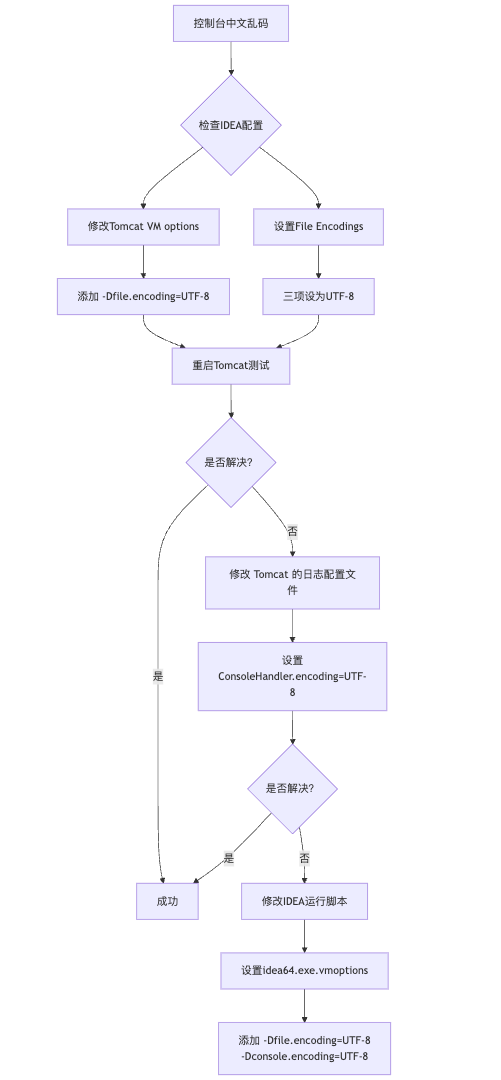
IDEA运行Tomcat出现乱码问题解决汇总
最近正值期末周,有很多同学在写期末Java web作业时,运行tomcat出现乱码问题,经过多次解决与研究,我做了如下整理:
原因:
IDEA本身编码与tomcat的编码与Windows编码不同导致,Windows 系统控制台…
利用最小二乘法找圆心和半径
#include <iostream>
#include <vector>
#include <cmath>
#include <Eigen/Dense> // 需安装Eigen库用于矩阵运算 // 定义点结构
struct Point { double x, y; Point(double x_, double y_) : x(x_), y(y_) {}
}; // 最小二乘法求圆心和半径 …
使用docker在3台服务器上搭建基于redis 6.x的一主两从三台均是哨兵模式
一、环境及版本说明
如果服务器已经安装了docker,则忽略此步骤,如果没有安装,则可以按照一下方式安装: 1. 在线安装(有互联网环境): 请看我这篇文章 传送阵>> 点我查看 2. 离线安装(内网环境):请看我这篇文章 传送阵>> 点我查看
说明:假设每台服务器已…
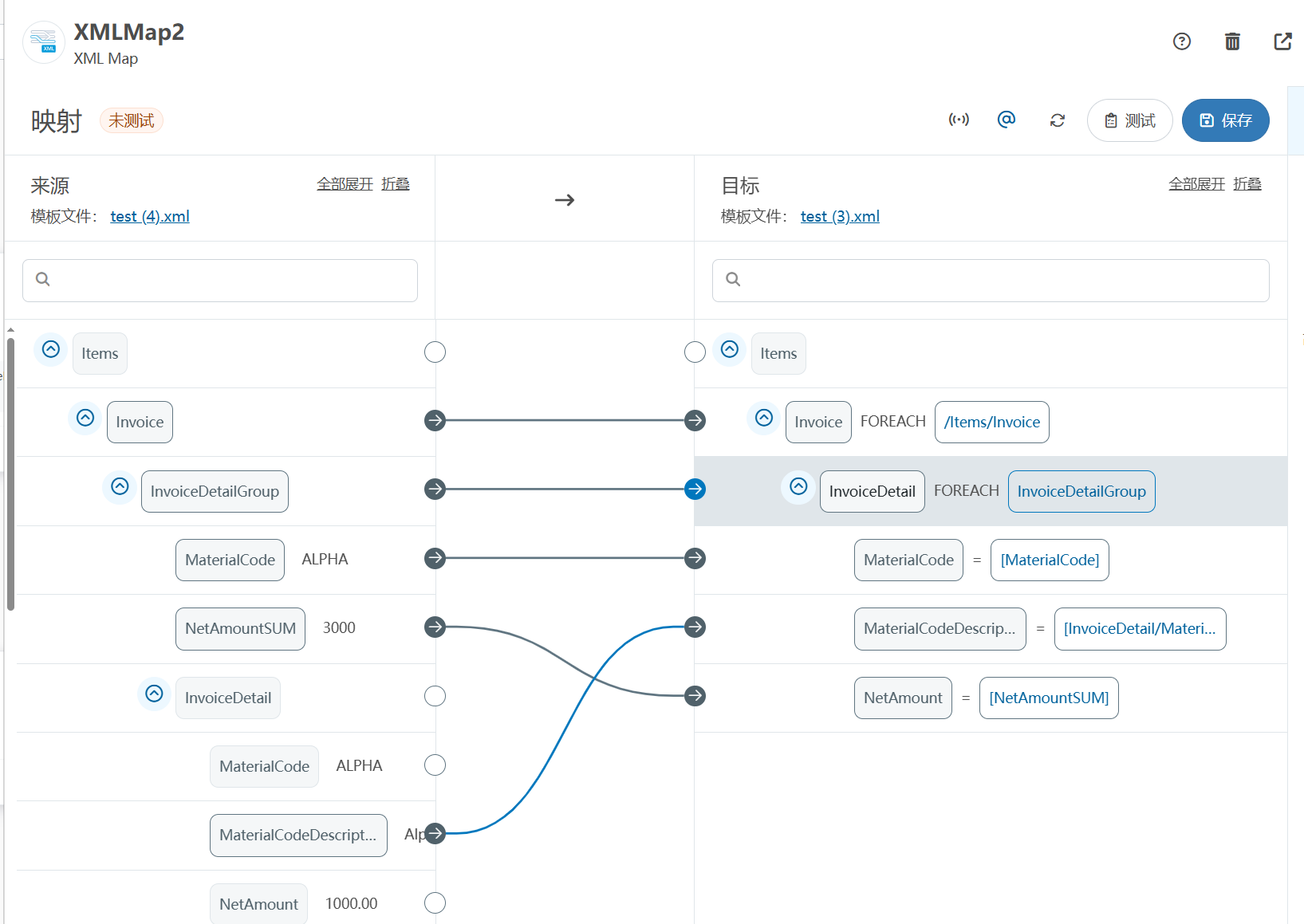
XML Group端口详解
在XML数据映射过程中,经常需要对数据进行分组聚合操作。例如,当处理包含多个物料明细的XML文件时,可能需要将相同物料号的明细归为一组,或对相同物料号的数量进行求和计算。传统实现方式通常需要编写脚本代码,增加了开…
LBE-LEX系列工业语音播放器|预警播报器|喇叭蜂鸣器的上位机配置操作说明
LBE-LEX系列工业语音播放器|预警播报器|喇叭蜂鸣器专为工业环境精心打造,完美适配AGV和无人叉车。同时,集成以太网与语音合成技术,为各类高级系统(如MES、调度系统、库位管理、立库等)提供高效便捷的语音交互体验。
L…
(LeetCode 每日一题) 3442. 奇偶频次间的最大差值 I (哈希、字符串)
题目:3442. 奇偶频次间的最大差值 I 思路 :哈希,时间复杂度0(n)。 用哈希表来记录每个字符串中字符的分布情况,哈希表这里用数组即可实现。
C版本:
class Solution {
public:int maxDifference(string s) {int a[26]…
【大模型RAG】拍照搜题技术架构速览:三层管道、两级检索、兜底大模型
摘要
拍照搜题系统采用“三层管道(多模态 OCR → 语义检索 → 答案渲染)、两级检索(倒排 BM25 向量 HNSW)并以大语言模型兜底”的整体框架: 多模态 OCR 层 将题目图片经过超分、去噪、倾斜校正后,分别用…
【Axure高保真原型】引导弹窗
今天和大家中分享引导弹窗的原型模板,载入页面后,会显示引导弹窗,适用于引导用户使用页面,点击完成后,会显示下一个引导弹窗,直至最后一个引导弹窗完成后进入首页。具体效果可以点击下方视频观看或打开下方…
接口测试中缓存处理策略
在接口测试中,缓存处理策略是一个关键环节,直接影响测试结果的准确性和可靠性。合理的缓存处理策略能够确保测试环境的一致性,避免因缓存数据导致的测试偏差。以下是接口测试中常见的缓存处理策略及其详细说明:
一、缓存处理的核…
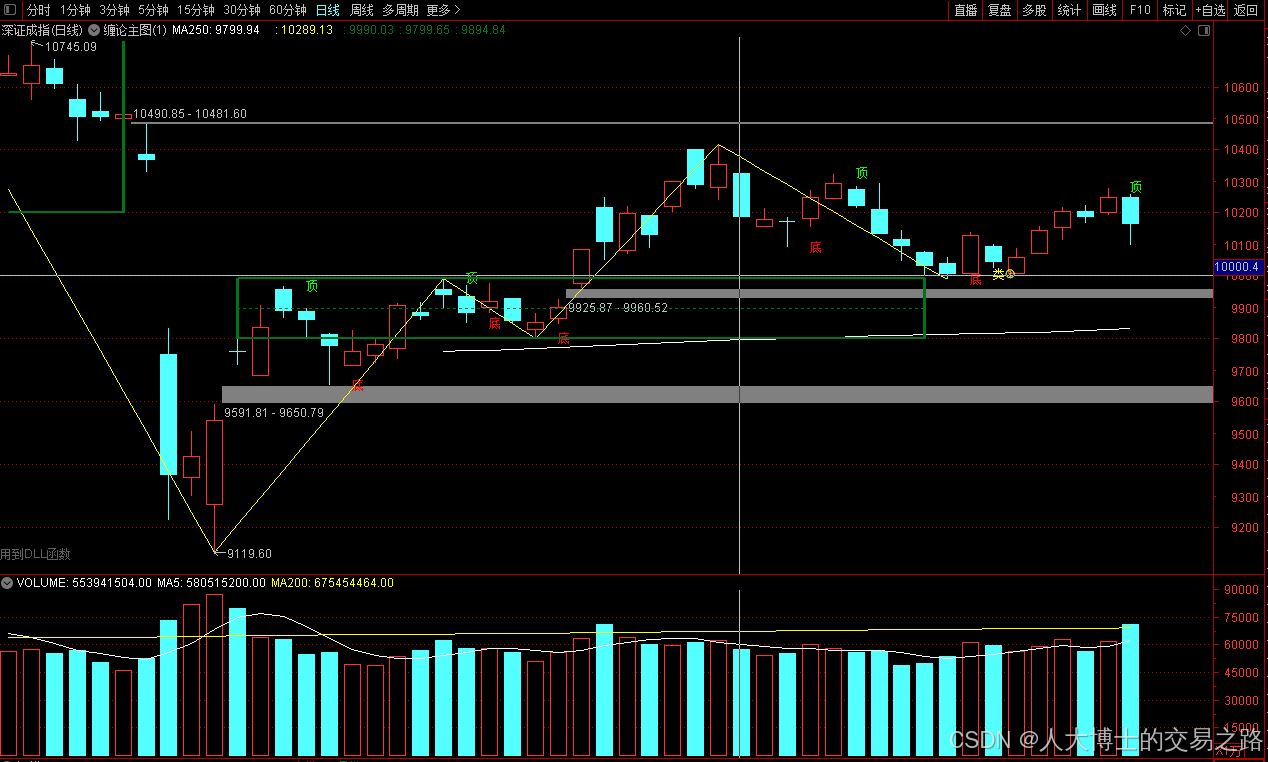
龙虎榜——20250610
上证指数放量收阴线,个股多数下跌,盘中受消息影响大幅波动。 深证指数放量收阴线形成顶分型,指数短线有调整的需求,大概需要一两天。 2025年6月10日龙虎榜行业方向分析 1. 金融科技
代表标的:御银股份、雄帝科技
驱动…
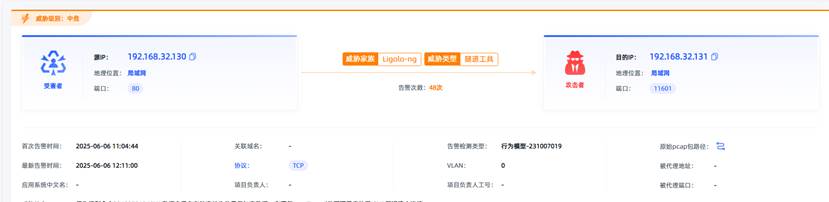
观成科技:隐蔽隧道工具Ligolo-ng加密流量分析
1.工具介绍
Ligolo-ng是一款由go编写的高效隧道工具,该工具基于TUN接口实现其功能,利用反向TCP/TLS连接建立一条隐蔽的通信信道,支持使用Let’s Encrypt自动生成证书。Ligolo-ng的通信隐蔽性体现在其支持多种连接方式,适应复杂网…
铭豹扩展坞 USB转网口 突然无法识别解决方法
当 USB 转网口扩展坞在一台笔记本上无法识别,但在其他电脑上正常工作时,问题通常出在笔记本自身或其与扩展坞的兼容性上。以下是系统化的定位思路和排查步骤,帮助你快速找到故障原因:
背景:
一个M-pard(铭豹)扩展坞的网卡突然无法识别了,扩展出来的三个USB接口正常。…
未来机器人的大脑:如何用神经网络模拟器实现更智能的决策?
编辑:陈萍萍的公主一点人工一点智能 未来机器人的大脑:如何用神经网络模拟器实现更智能的决策?RWM通过双自回归机制有效解决了复合误差、部分可观测性和随机动力学等关键挑战,在不依赖领域特定归纳偏见的条件下实现了卓越的预测准…
Linux应用开发之网络套接字编程(实例篇)
服务端与客户端单连接
服务端代码
#include <sys/socket.h>
#include <sys/types.h>
#include <netinet/in.h>
#include <stdio.h>
#include <stdlib.h>
#include <string.h>
#include <arpa/inet.h>
#include <pthread.h>
…
华为云AI开发平台ModelArts
华为云ModelArts:重塑AI开发流程的“智能引擎”与“创新加速器”!
在人工智能浪潮席卷全球的2025年,企业拥抱AI的意愿空前高涨,但技术门槛高、流程复杂、资源投入巨大的现实,却让许多创新构想止步于实验室。数据科学家…
深度学习在微纳光子学中的应用
深度学习在微纳光子学中的主要应用方向
深度学习与微纳光子学的结合主要集中在以下几个方向:
逆向设计 通过神经网络快速预测微纳结构的光学响应,替代传统耗时的数值模拟方法。例如设计超表面、光子晶体等结构。
特征提取与优化 从复杂的光学数据中自…