1. 简介
ATACseq (Assay for Transposase-Accessible Chromatin using sequencing) 使用转座酶在测序前有效地片段化可访问的 DNA(DNA可极性)。结果提供了一种绘制可访问/开放染色质基因组范围的方法。
与其他技术相比,ATACseq 有几个优点,包括:
-
所需输入材料少(> 10,000 个细胞) -
实验所需时间短(约 4 小时)
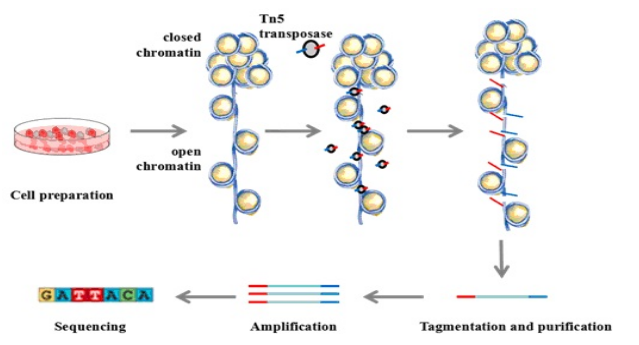
2. 酶
-
下面介绍几种不同酶获取数据的差异
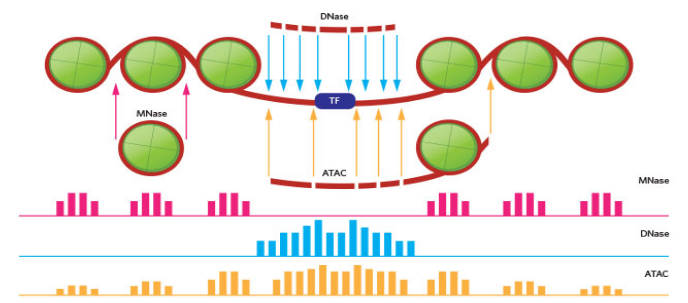
-
DNaseseq- 酶消化以从转录因子结合位点周围的开放染色质中提取信号。 -
MNaseseq- 酶消化以提取代表核小体定位的信号。 -
ATACseq- 使用转座酶并提供一种 同时从单个样本的转录因子结合位点和核小体位置提取信号的方法。
3. Work
在本教程[1]中,我们将使用一些公开的数据来了解 R 中 ATACseq 处理的一些基础知识。
将研究 ATACseq 数据在 TSS 上的比对、比对后处理和绘图。
4. 数据
本教程中,我们将使用三组已发布的数据。
4.1. data_1
第一个数据集来自原始 ATACseq 论文[2]。我们将使用 ATACseq_50k_Rep2 示例 GEO - GSM1155958 可以从 ENA 以 FASTQ 格式获取数据。
-
SAMN02192806 - [here](https://www.ebi.ac.uk/ena/data/view/SAMN02192806 “SAMN02192806”)
4.2. data_2
对于第二个数据集,我们将 UCSD 的 Bing Ren 生成的 ATACseq 作为 ENCODE 联盟的一部分。它包括来自小鼠几种组织的样本。数据和示例信息的链接包含在下面的列表中。
-
Liver day 12 - ENCSR302LIV [3] -
Kidney day 15 - ENCSR023QZX [4] -
Hindbrain day 12 - ENCSR088UYE [5]
4.3. data_3
最后,我完全按照本次教程中的描述处理了来自 MSKCC 的 Christina Leslie 实验室的一些数据,因此我们可以在练习中回顾 ATACseq 数据的一些特征以及 ENCODE 管道处理的相同数据。
原始数据和处理后的 BAM 文件可从 ENCODEs 门户网站获得
-
T-Reg - [ENCSR724UJS](https://www.encodeproject.org/experiments/ENCSR724UJS/ “ENCSR724UJS”)
FQ 文件可以在此处找到 read1[6] 和此处的 read2[7]。我们还将使用对齐数据作为BAM[8] 文件,该文件可在此处找到。
5. 参考数据
对于 ATACseq 分析,我们需要一些参考数据。
-
fasta格式的参考基因组——我们将从BSGenome Bioconductor注释包中检索。 -
基因模型——我们将从 TxDb Bioconductor注释包中检索这些模型。 -
Blacklists 特定于基因组的区域。这些可以在此处的 ENCODE 门户 [9]中找到
6. 已处理数据
我们从以下链接中的公共测序数据开始,并使用 Bioconductor 中的参考数据。由于其中一些处理步骤可能需要一点时间,因此我提供了指向预处理结果的链接。
来自我们对齐/排序/索引的 BAM 文件和 BAI 索引:
-
SAMN02192806 - Greenleaf BAM - Greenleaf示例的完整BAM文件在我们的Rsubread对齐、排序和索引中生成。 -
SAMN02192806 - Greenleaf BAI index - Greenleaf示例中BAM的BAI索引文件在我们的对齐、排序和索引中生成如下。
小型 BAM、peak calls 和目录结构。
-
ATAC_Workshop_Essential.zip - 需要额外的文件和目录结构。
下载上述文件并解压缩 ATAC_Workshop.zip 后,您应该将 Sorted_ATAC_50K_2.bam 和 Sorted_ATAC_50K_2.bam.bai 文件移动到 ATAC_Workshop/ATAC_Data/ATAC_BAM/ 。您还应该将 RU_ATAC_Workshop.Rmd 复制到 ATAC_Workshop/ 目录,然后打开以确保所有相对路径都是正确的。
与上述相同,但具有用于计数的 BAM 以及小型 BAM、peak calls 和目录结构。
-
Bigwigs - 在 IGV 中审查的 BigWigs. -
ATAC_Workshop.zip - 附加文件和目录结构。
欢迎Star -> 学习目录
更多教程 -> 转录组测序分析教程合集
更多教程 -> 单细胞系列教程:合集
参考资料
Source: https://rockefelleruniversity.github.io/RU_ATACseq/presentations/singlepage/RU_ATAC.html
[2]first dataset: https://pubmed.ncbi.nlm.nih.gov/24097267/
[3]ENCSR302LIV: https://www.encodeproject.org/experiments/ENCSR302LIV/
[4]ENCSR023QZX: https://www.encodeproject.org/experiments/ENCSR023QZX/
[5]ENCSR088UYE: https://www.encodeproject.org/experiments/ENCSR088UYE/
[6]read1: https://www.encodeproject.org/files/ENCFF175VOD/@@download/ENCFF175VOD.fastq.gz
[7]read2: https://www.encodeproject.org/files/ENCFF447BGX/@@download/ENCFF447BGX.fastq.gz
[8]BAM: https://www.encodeproject.org/files/ENCFF053CGD/@@download/ENCFF053CGD.bam
[9]ENCODE portal: https://www.encodeproject.org/annotations/ENCSR636HFF/
本文由 mdnice 多平台发布